新技术分析单细胞的染色质构象
分析染色质构象的技术不少,但有的需要大量细胞,有的则分辨率太低。这阻碍了我们对于单细胞中染色质构象的了解。近日,瑞典卡罗林斯卡学院的研究人员在《Biotechniques》上介绍了一种新方法,能够高分辨率地分析单细胞中染色质的接近程度。
对于理解基因调控、DNA复制和修复来说,研究染色体的结构性质和空间组织尤为重要。染色质构象捕获(3C)技术在近年来被广泛使用,并衍生出更多技术,如4C、5C和Hi-C。3C技术利用甲醛来交联染色质,在酶切消化后原位连接,并以高通量的方式来评估染色质纤维的接近程度。这种方法分辨率高,但需要大量细胞。相反,DNA FISH可实现单细胞的研究,但3-D分辨率较低。
在这篇文章中,研究人员介绍了一种新方法,名为ChrISP(chromatin in situ proximity)。它不仅能够以高于显微镜的分辨率探索染色质纤维的接近程度,还能对细胞群体中这一特征的频率进行分析。这种新方法利用原位邻位连接分析(ISPLA)的特点,但不需要滚环扩增(RCA)。因此,它克服了细胞核亚结构所带来的空间位阻,提供了连续的信号。
以地高辛或生物素标记的DNA探针与甲醛固定的细胞杂交,接着是一抗检测。当带有不同寡核苷酸DNA序列的二抗与一抗结合时,添加骨架(长接头)和荧光标记的碎片(短接头)寡核苷酸。如果两个不同二抗之间的距离小于170Å,则它们各自的寡核苷酸足够靠近,让骨架和碎片寡核苷酸可同时连接,并最终形成一个荧光标记的环状DNA分子。
作者认为,与现有技术相比,ChrISP的分辨率有了大大的提升。STED、PALM成像在视场和荧光选择上存在限制,且第三维度的分辨率不如传统的共聚焦显微镜。相比之下,ChrISP在三个维度的分辨率都可达17 nm,其轴向分辨率有30倍的改善。
利用ChrISP方法,研究人员在单细胞水平记录了染色质区域的特点。他们认为,这种方法能够灵活应用在多个方面,例如在转录、RNA剪接和DNA复制过程中如研究染色质结构及相关标记。
-
科技前沿
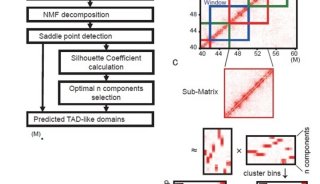
-
项目成果