查看完整版本请点击这里:
【求助】表达PCR扩增问题
大家帮我看看【求助】表达PCR扩增问题
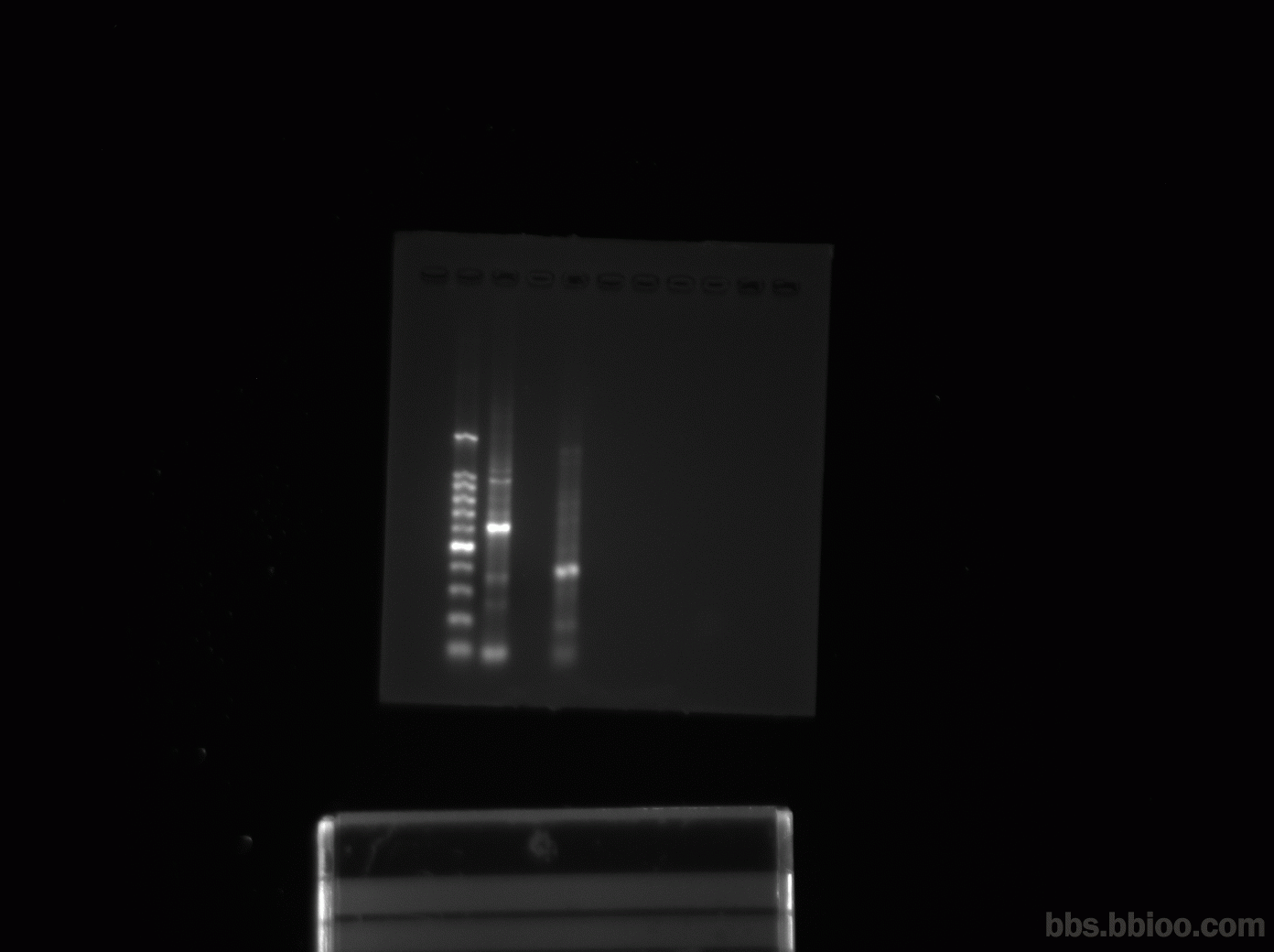
maker 旁边的是带酶切位点的引物 远的那个是同样的引物不带酶切位点。
我扩的是全长 1074bp,100bp的marker 亮的位置是600。
为什么得不到我的目的条带呢,我是用我得到序列开放阅读框的两端设计的引物。
查看完整版本请点击这里:
【求助】表达PCR扩增问题
【求助】表达PCR扩增问题
2012.2.26.gif
字体: 小 中 大 | 打印 发表于: 2015-4-02 20:33 作者: 98776langtao 来源: 分析测试百科网

2012.2.26.gif
最新回复
爬呀爬 (2015-4-02 20:34:08)
marker旁边的条带600bp亮度很大,说明发生的错配严重,建议你做个降落PCR,退火温度设定的高一点。还是不好的话,就只能换一对引物了,引物不一定非在开放阅读框架两端
邀月 (2015-4-02 20:34:29)
能不能把你的序列和引物发上来看看,或者PM我
98776langtao (2015-4-02 20:34:56)
98776langtao (2015-4-02 20:35:17)
QUOTE:
我提高退火温度做了 63-57度的每个温度5个循环 结果只剩下引物二聚体了。并从57-51退火600bp的还在。确实我的这两条引物都存在错配的情况,但是 我表达全长,只能把引物设计在开放阅读框的两端呀。该怎么办呢,把引物变长是不是就能解决呢??remonte (2015-4-02 20:35:39)
QUOTE:
设计的引物扩增片段可以大于1047,你要全基因只要把ATG和终止密码子包括在内就行applebook=213 (2015-4-02 20:35:58)
1.你的酶切位点的保护碱基设计的不合理,你可以参考NEB的酶切位点保护碱基表;
2.我下载你的附件了,你的引物设计的不论是特异性还是稳定性上都不好,里面提示你:你的Forward Primer的3'端有很严重的False Priming,而且形成的双链的ΔG =-11.0 [kcals/mol] ,退火后的双链比较稳定,很容易引起错误的聚合反应,正向引物会造出338bp的副产物,你的Marker应该是TaKaRa 100bp的吧?挨着Marker的那个样好像就有这个副产物。
3.你的Reverse Primer也不合格,3'端也有很严重的False Priming,形成的双链的ΔG =-16.2 [kcals/mol] ,退火后的双链比正向引物造出的那个还稳定,这个会造成777bp的副产物,挨着Marker的那个样的最亮的应该就是。
4.建议你重新设计引物,把引物的长度设计在26~32bp,直接两步PCR扩增就行了;或者你做TD-PCR,你现在的两条引物的Tm值都不到57℃,你在63~57℃是比较难成功的,引物最好以G\C结尾,但是3'末端的GC也别太多,容易造成非特异性扩增;
5.好像挨着Marker的那个样有你需要的产物,就是太少。
希望对你有帮助
131415 (2015-4-02 20:36:22)
正向引物会造出338bp的副产物,??这个你怎么知道的?
veiwu (2015-4-02 20:36:46)
ΔG =-16.2 ?、这是什么值最好。多多请教
【求助】表达PCR扩增问题