诚信认证:
工商注册信息已核实! 扫一扫即可访问手机版展台
扫一扫即可访问手机版展台
「青莲百奥干货」蛋白注释利器Uniprot的玩法!
近日有粉丝向小编求生信科普文章,怎奈我们生信团队过于忙碌,无暇安排,小编为了满足粉丝要求也是无所不用其极,生信大师兄终于被我的良(ku)苦(kou)用(po)心而感动,加班赶制这篇Uniprot数据库的应用文章,快来一起学习吧!

Uniprot(https://www.uniprot.org/)是信息丰富、资源广的蛋白质序列数据库,整合Swiss-Prot、TrEMBL 和 PIR 三大数据库的数据而成。怎样用uniprot对需要的蛋白进行注释呢?那我们就用uniprot数据库对一些微生物蛋白进行分型,找到这些蛋白对应的界门纲目科属种的注释信息。
首先,打开uniprot数据库的网站,找到ID mapping。

进入IDmapping后,把需要注释的蛋白id导入Provide your identifiers里面。Select options选择默认选项就可以。导入蛋白完成后,点击Submit。

其次,等网站注释完成后,会跳转到蛋白注释页面,里面有一些蛋白的基本注释结果,比如entry,entryname,genename,length等等注释。没有我们需要的分型注释。下面就需要我们把需要的注释信息调出来。点击columns;

![]()
比较重要的有蛋白,序列,长度,功能,表达,亚细胞,GO,标志物等等大量的注释信息。还有关联的string蛋白互作数据库,ensemble数据库等等常用数据库。

点击选择界(Kingdom)、门(Phylum)、纲(Class)、目(Order)、科(Family)、属(Genus)、种(Species)。然后点击右上角的SAVE进行保存。
保存完毕后,网页会自动跳转到注释结果页面,里面就会显示刚才勾选的注释信息。
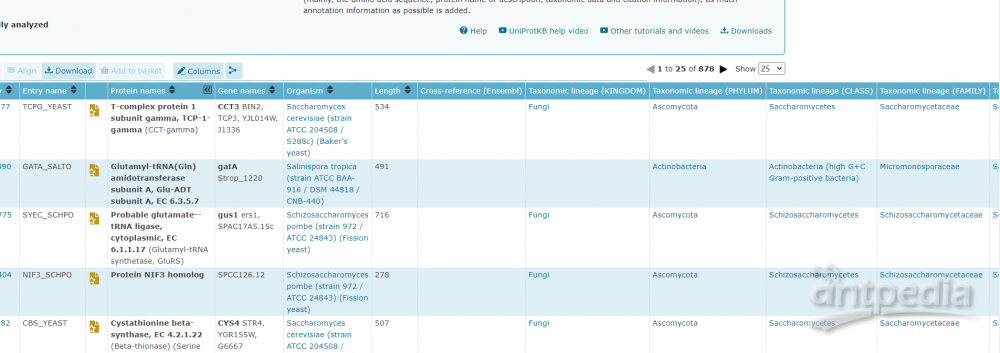
这些蛋白的所在的生物分类就可以一目了然了。
当然,如果还想需要其他的注释信息,可以根据自己的需求,勾选需要的,去掉不需要的。得到了需要的注释信息,我们可以把注释信息下载下来,下面推荐excel格式的。

下载到本地后的数据格式为:

总结