3D单分子荧光成像系统-SAFe 360
SAFe 360是法国abbelight公司推出的一款基于单分子定位的显微成像(SMLM)的新型3D单分子成像系统,它独有的DAISY技术整合了散光技术和超临界角光技术,能够极大提高定位精度,xyz三轴定位精度高达15nm,可以提供高清晰三维亚细胞结构图像,支持同时四色成像,可以用于细胞纳米三维成像,观测高清晰亚细胞器结构,实时研究不同的结构功能蛋白的共定位信息,在单分子水平研究分子动力学反应以及细胞间的相互作用等。
| 加装 | TIRF PALM STORM SPT smFRET ...... | 兼容 | Confocal Spinning-Desk Widefield SIM STED ...... |
设备参数
+ 成像模式:PALM、STORM、PAINT、smFRET 、SPT
+ 光源模式:Epi、TIRF、HILO
+ 最高分辨率:15 nm的XYZ轴分辨率
+ 超大视野:200 × 200 μm2的视野
+ 一次可同时采集1.2 μm深度图像信息
+ 最高图像深度:10 μm
+ 实时漂移矫正
+ 最高四色同时成像
+ 活细胞成像模式
配套试剂
Smart kit • 10 doses per box • 200 µL per dose • 30 sec prepartion • 2 months in a fridge • 2 weeks on sample | Compatible dyes • Atto 488, WGA-AF®488 • AF®532, CF®532, Cy3b • AF®555, AF®594, CF®555, AF®568, CF®568, Cy5, MemBriteTM 568, TMR • AF®647, CF®647, AF®680, CF®680, MemBriteTM 640, Actin-stain 670, SiR647 |
应用案例
研究细胞质膜上的内陷结构与功能
真核细胞的细胞质膜是一个不均一体系,包含大量脂类组成和生物物理特性不同的区域。这些蛋白脂类区域使质膜产生内陷,而内陷在胞吞过程中起重要作用。在这些质膜区域中,网格蛋白包被的小窝(clathin coated pits, CCP)和胞膜窖(caveolae)由于表面有明显的蛋白包被,很容易用电镜成像等方法观测到。CCP呈80-120 nm的球形结构,包被有网格蛋白和衔接蛋白。网格蛋白调控的内吞作用通路(CME)通过被膜小窝实现胞吞。Caveolae是50-80 nm的内陷结构,在信号转导,膜运输,胆固醇运输,机械传感等过程中起作用,在受到机械应力作用的细胞,如脂肪细胞,内皮细胞和肌细胞中含量较高。有研究发现了小凹的产生及与胞内体的融合,但Caveolae是否在胞吞中起作用尚无定论。
在下图的实例中,研究人员使用了Abbelight的成像3D单分子荧光成像系统-SAFe 360分辨出了内皮细胞中的Clathrin和Caveolae。结果显示了清晰、无重叠的荧光分布,与电镜成像结果一致。

图1. Abbelight SAFe360系统重现质膜上蛋白脂类区域的蛋白分布

图2. 通过SAFe360的同时多色成像功能可以清晰、无重叠地区分Clathrin 和Caveolae,进一步研究Clathrin 和Caveolae的内吞作用通路的相互关系。
■ 研究大肠杆菌RNA聚合酶的空间分布与动力学
大肠杆菌中的RNA聚合酶(RNAP)空间上呈拟核形状分布,是核糖体RNA(rRNA)的转录中心。下方实例使用Abbelight SAFe 360系统通过PALM超分辨成像与单分子追踪(sptPALM)解析大肠杆菌RNAP的纳米尺度空间分布与动力学,进而研究转录调控机制。

图1. (A)Denndra2标记RNAP在大肠杆菌中分布定位(定位精度约为15 nm);(B)通过DBSCAN算法对大肠杆菌中RNA聚合酶分布进行团簇分析。

图2. 在活细胞中以200 FPS(5 ms/帧)的采集速度对大肠杆菌中Dendra2标记的RNAP分子进行单分子追踪以研究单个RNAP分子运动轨迹,按照运动状态分为静态(红色,即转录中)或动态(紫色,扩散运动)。
测试数据
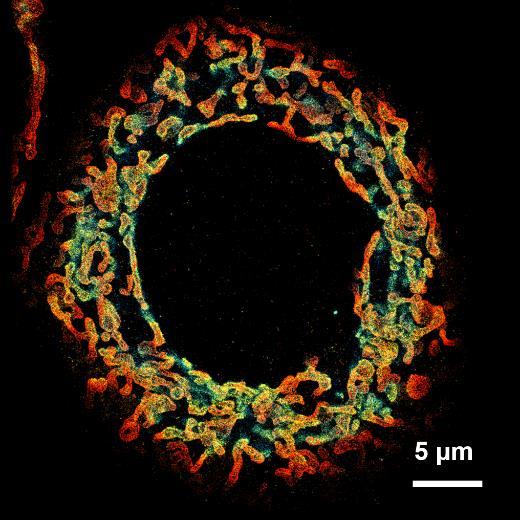
3D线粒体结构 |
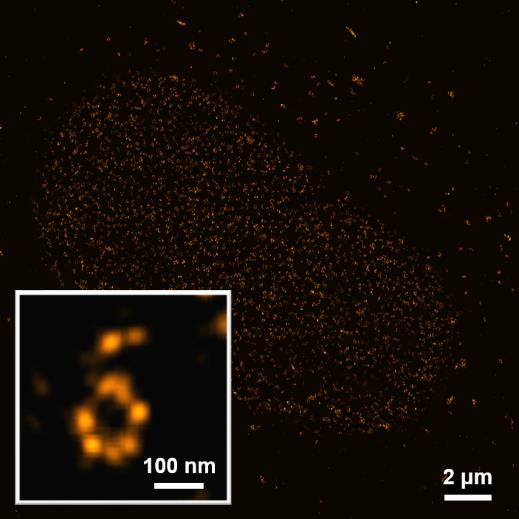
核孔复合物 |
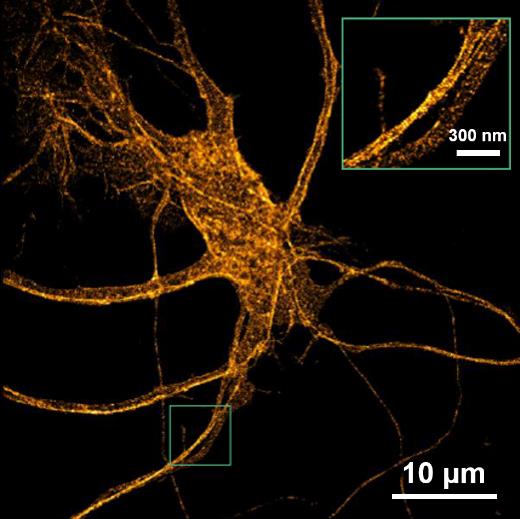
老鼠海马神经元 |
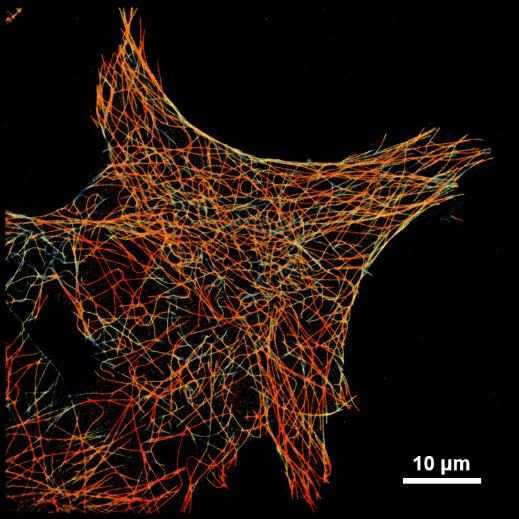
微管蛋白网络 |
发表文章
[1] Radhakrishnan, A. V., et al. “Single-Protein Tracking to Study Protein Interactions During Integrin-Based Migration.“ The Integrin Interactome. Humana, New York, NY, (2021). 85-113.
[2] Jouchet, Pierre, et al. “Nanometric axial localization of single fluorescent molecules with modulated excitation.“ Nature Photonics (2021): 1-8.
[3] Pernier, Julien, et al. “Myosin 1b flattens and prunes branched actin filaments.“ Journal of cell science 133.18 (2020).
[4] Jimenez, Angélique, Karoline Friedl, and Christophe Leterrier. “About samples, giving examples: optimized single molecule localization microscopy.“ Methods 174 (2020): 100-114.
[5] Mau, Adrien, et al. “Fast scanned widefield scheme provides tunable and uniform illumination for optimized SMLM on large fields of view.“ bioRxiv (2020).
[6] Orre, Thomas, et al. “Molecular motion and tridimensional nanoscale localization of kindlin control integrin activation in focal adhesions.“ bioRxiv (2020).
[7] Cabriel, Clément, et al. “Combining 3D single molecule localization strategies for reproducible bioimaging.“ Nature communications 10.1 (2019): 1980.
[8] Woodhams, Stephen G., et al. “Cell type–specific super-resolution imaging reveals an increase in calcium-permeable AMPA receptors at spinal peptidergic terminals as an anatomical correlate of inflammatory pain.“ Pain 160.11 (2019): 2641-2650.
[9] Belkahla, Hanen, et al. “Carbon dots, a powerful non-toxic support for bioimaging by fluorescence nanoscopy and eradication of bacteria by photothermia.“ Nanoscale Advances (2019).
[10] Denis, Kevin, et al. “Targeting Type IV pili as an antivirulence strategy against invasive meningococcal disease.“ Nature microbiology 4.6 (2019): 972.
[11] Szabo, Quentin, et al. “TADs are 3D structural units of higher-order chromosome organization in Drosophila.“ Science advances 4.2 (2018): eaar8082.
[12] Boudjemaa, Rym, et al. “Impact of bacterial membrane fatty acid composition on the failure of daptomycin to kill Staphylococcus aureus.“ Antimicrobial agents and chemotherapy 62.7 (2018): e00023-18.
[13] Culley, Siân, et al. “Quantitative mapping and minimization of super-resolution optical imaging artifacts.“ Nature methods 15.4 (2018): 263.
[14] Berger, Stephen L., et al. “Localized myosin II activity regulates assembly and plasticity of the axon initial segment.“ Neuron 97.3 (2018): 555-570.
[15] Cabriel, Clément, et al. “Aberration-accounting calibration for 3D single-molecule localization microscopy.“ Optics letters 43.2 (2018): 174-177.
[16] Bouissou, Anaïs, et al. “Podosome force generation machinery: a local balance between protrusion at the core and traction at the ring.“ ACS nano 11.4 (2017): 4028-4040.
[17] Sellés, Julien, et al. “Nuclear pore complex plasticity during developmental process as revealed by super-resolution microscopy.“ Scientific reports 7.1 (2017): 14732.
[18] Bourg, Nicolas, et al. “Direct optical nanoscopy with axially localized detection.“ Nature Photonics 9.9 (2015): 587.
用户单位
|
|
|
|
|
|
|
|
|
除厂家/中国总经销商外,我们找不到
3D单分子荧光成像系统-SAFe 360 的一般经销商信息,有可能该产品在中国没有其它经销商。
如果您是,请告诉我们,我们的邮件地址是:sales@antpedia.net 请说明: 1.产品名称 2.公司介绍 3.联系方式 |
售后服务
我会维修/培训/做方法
如果您是一名工程师或者专业维修科学 仪器的服务商,都可参与登记,我们的平台 会为您的服务精确的定位并展示。