三代测序技术和原理介绍(二)
Solid技术
Solid测序技术是ABI公司于2007年开始投入用于商业测序应用的仪器。它基于连接酶法,即利用DNA连接酶在连接过程之中测序(图6)2,4。它的原理是:
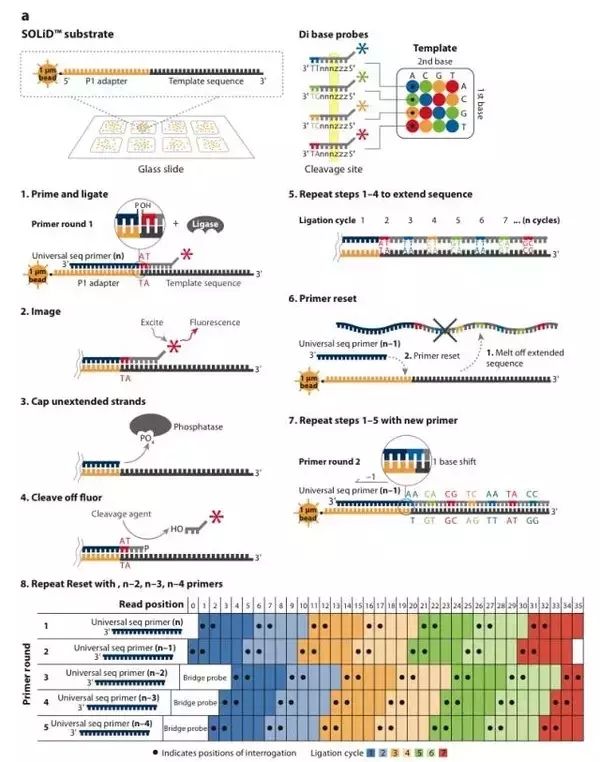
图6-a. Solid测序技术
(1)DNA文库构建
片段打断并在片段两端加上测序接头,连接载体,构建单链DNA文库。
(2)Emulsion PCR
Solid的PCR过程也和454的方法类似,同样采用小水滴emulsion PCR,但这些微珠比起454系统来说则要小得多,只有1um。在扩增的同时对扩增产物的3’端进行修饰,这是为下一步的测序过程作的准备。3’修饰的微珠会被沉积在一块玻片上。在微珠上样的过程中,沉积小室将每张玻片分成1个、4个或8个测序区域(图6-a)。Solid系统最大的优点就是每张玻片能容纳比454更高密度的微珠,在同一系统中轻松实现更高的通量。
(3)连接酶测序
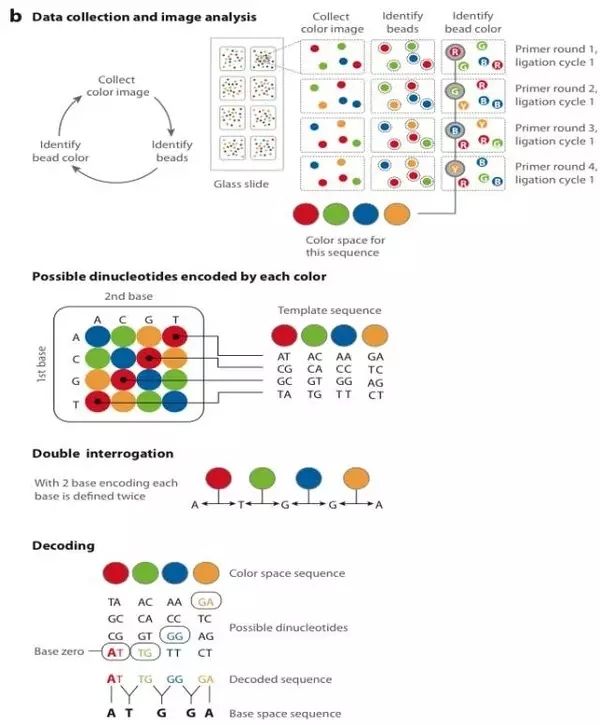
这一步是Solid测序的独特之处。它并没有采用以前测序时所常用的DNA聚合酶,而是采用了连接酶。Solid连接反应的底物是8碱基单链荧光探针混合物,这里将其简单表示为:3’-XXnnnzzz-5’。连接反应中,这些探针按照碱基互补规则与单链DNA模板链配对。探针的5’末端分别标记了CY5、Texas Red、CY3、6-FAM这4种颜色的荧光染料(图6-a)。这个8碱基单链荧光探针中,第1和第2位碱基(XX)上的碱基是确定的,并根据种类的不同在6-8位(zzz)上加上了不同的荧光标记。这是Solid的独特测序法,两个碱基确定一个荧光信号,相当于一次能决定两个碱基。这种测序方法也称之为两碱基测序法。当荧光探针能够与DNA模板链配对而连接上时,就会发出代表第1,2位碱基的荧光信号,图6-a和图6-b中的比色版所表示的是第1,2位碱基的不同组合与荧光颜色的关系。在记录下荧光信号后,通过化学方法在第5和第6位碱基之间进行切割,这样就能移除荧光信号,以便进行下一个位置的测序。不过值得注意的是,通过这种测序方法,每次测序的位置都相差5位。即第一次是第1、2位,第二次是第6、7位……在测到末尾后,要将新合成的链变性,洗脱。接着用引物n-1进行第二轮测序。引物n-1与引物n的区别是,二者在与接头配对的位置上相差一个碱基(图6-a. 8)。也即是,通过引物n-1在引物n的基础上将测序位置往3’端移动一个碱基位置,因而就能测定第0、1位和第5、6位……第二轮测序完成,依此类推,直至第五轮测序,最终可以完成所有位置的碱基测序,并且每个位置的碱基均被检测了两次。该技术的读长在2×50bp,后续序列拼接同样比较复杂。由于双次检测,这一技术的原始测序准确性高达99.94%,而15x覆盖率时的准确性更是达到了99.999%,应该说是目前第二代测序技术中准确性最高的了。但在荧光解码阶段,鉴于其是双碱基确定一个荧光信号,因而一旦发生错误就容易产生连锁的解码错误。
图6-b. Solid测序技术
第三代测序技术
测序技术在近两三年中又有新的里程碑。以PacBio公司的SMRT和Oxford Nanopore Technologies纳米孔单分子测序技术,被称之为第三代测序技术。与前两代相比,他们最大的特点就是单分子测序,测序过程无需进行PCR扩增。
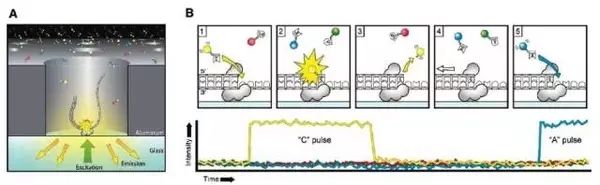
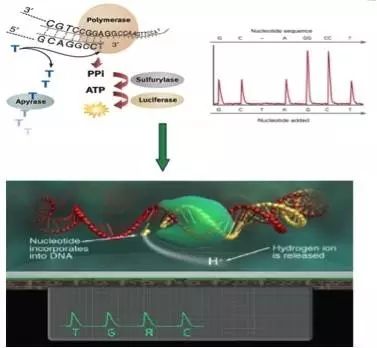
其中PacBio SMRT技术其实也应用了边合成边测序的思想5,并以SMRT芯片为测序载体。基本原理是: DNA聚合酶和模板结合,4色荧光标记 4 种碱基(即是dNTP),在碱基配对阶段,不同碱基的加入,会发出不同光,根据光的波长与峰值可判断进入的碱基类型。同时这个 DNA 聚合酶是实现超长读长的关键之一,读长主要跟酶的活性保持有关,它主要受激光对其造成的损伤所影响。PacBio SMRT技术的一个关键是怎样将反应信号与周围游离碱基的强大荧光背景区别出来。他们利用的是ZMW(零模波导孔)原理:如同微波炉壁上可看到的很多密集小孔。小孔直径有考究,如果直径大于微波波长,能量就会在衍射效应的作用下穿透面板而泄露出来,从而与周围小孔相互干扰。如果孔径小于波长,能量不会辐射到周围,而是保持直线状态(光衍射的原理),从而可起保护作用。同理,在一个反应管(SMRTCell:单分子实时反应孔)中有许多这样的圆形纳米小孔, 即 ZMW(零模波导孔),外径 100多纳米,比检测激光波长小(数百纳米),激光从底部打上去后不能穿透小孔进入上方溶液区,能量被限制在一个小范围(体积20X 10-21 L)里,正好足够覆盖需要检测的部分,使得信号仅来自这个小反应区域,孔外过多游离核苷酸单体依然留在黑暗中,从而实现将背景降到最低。另外,可以通过检测相邻两个碱基之间的测序时间,来检测一些碱基修饰情况,既如果碱基存在修饰,则通过聚合酶时的速度会减慢,相邻两峰之间的距离增大,可以通过这个来之间检测甲基化等信息(图7)。SMRT技术的测序速度很快,每秒约10个dNTP。但是,同时其测序错误率比较高(这几乎是目前单分子测序技术的通病),达到15%,但好在它的出错是随机的,并不会像第二代测序技术那样存在测序错误的偏向,因而可以通过多次测序来进行有效的纠错。
图7.PacBio SMRT测序原理
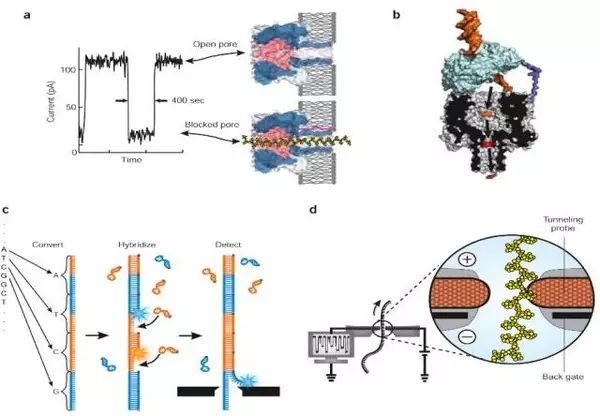
Oxford Nanopore Technologies公司所开发的纳米单分子测序技术与以往的测序技术皆不同,它是基于电信号而不是光信号的测序技术5。该技术的关键之一是,他们设计了一种特殊的纳米孔,孔内共价结合有分子接头。当DNA碱基通过纳米孔时,它们使电荷发生变化,从而短暂地影响流过纳米孔的电流强度(每种碱基所影响的电流变化幅度是不同的),灵敏的电子设备检测到这些变化从而鉴定所通过的碱基(图8)。
该公司在去年基因组生物学技术进展年会(AGBT)上推出第一款商业化的纳米孔测序仪,引起了科学界的极大关注。纳米孔测序(和其他第三代测序技术)有望解决目前测序平台的不足,纳米孔测序的主要特点是:读长很长,大约在几十kb,甚至100 kb;错误率目前介于1%至4%,且是随机错误,而不是聚集在读取的两端;数据可实时读取;通量很高(30x人类基因组有望在一天内完成);起始DNA在测序过程中不被破坏;以及样品制备简单又便宜。理论上,它也能直接测序RNA。
纳米孔单分子测序计算还有另一大特点,它能够直接读取出甲基化的胞嘧啶,而不必像传统方法那样对基因组进行bisulfite处理。这对于在基因组水平直接研究表观遗传相关现象有极大的帮助。并且改方法的测序准确性可达99.8%,而且一旦发现测序错误也能较容易地进行纠正。但目前似乎还没有应用该技术的相关报道。
图8. 纳米孔测序
其他测序技术
目前还有一种基于半导体芯片的新一代革命性测序技术——Ion Torrent6。该技术使用了一种布满小孔的高密度半导体芯片, 一个小孔就是一个测序反应池。当DNA聚合酶把核苷酸聚合到延伸中的DNA链上时,会释放出一个氢离子,反应池中的PH发生改变,位于池下的离子感受器感受到H+离子信号,H+离子信号再直接转化为数字信号,从而读出DNA序列(图9)。这一技术的发明人同时也是454测序技术的发明人之一——Jonathan Rothberg,它的文库和样本制备跟454技术很像,甚至可以说就是454的翻版,只是测序过程中不是通过检测焦磷酸荧光显色,而是通过检测H+信号的变化来获得序列碱基信息。Ion Torrent相比于其他测序技术来说,不需要昂贵的物理成像等设备,因此,成本相对来说会低,体积也会比较小,同时操作也要更为简单,速度也相当快速,除了2天文库制作时间,整个上机测序可在2-3.5小时内完成,不过整个芯片的通量并不高,目前是10G左右,但非常适合小基因组和外显子验证的测序。
小结
以上,对各代测序技术的原理做了简要的阐述,这三代测序技术的特点比较汇总在以下表1和表2中。其中测序成本,读长和通量是评估该测序技术先进与否的三个重要指标。第一代和第二代测序技术除了通量和成本上的差异之外,其测序核心原理(除Solid是边连接边测序之外)都是基于边合成边测序的思想。第二代测序技术的优点是成本较之一代大大下降,通量大大提升,但缺点是所引入PCR过程会在一定程度上增加测序的错误率,并且具有系统偏向性,同时读长也比较短。第三代测序技术是为了解决第二代所存在的缺点而开发的,它的根本特点是单分子测序,不需要任何PCR的过程,这是为了能有效避免因PCR偏向性而导至的系统错误,同时提高读长,并要保持二代技术的高通量,低成本的优点。
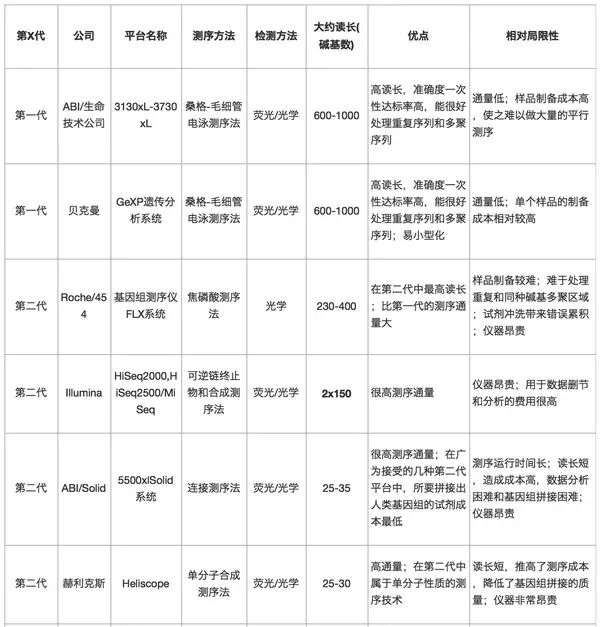
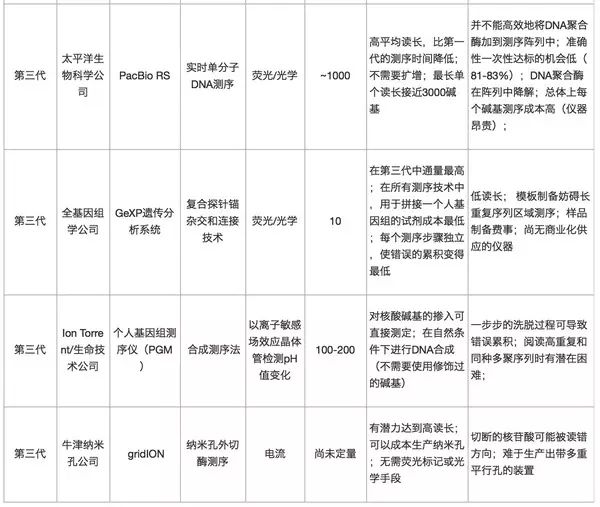
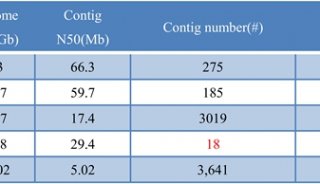
表1:测序技术的比较
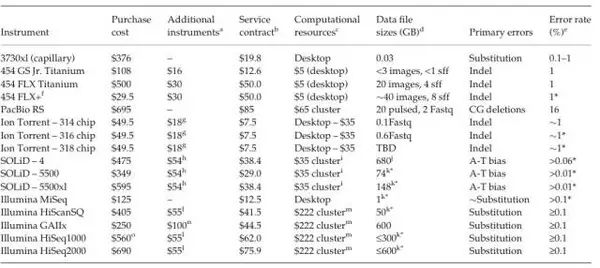
表2:主流测序机器的成本测序比较
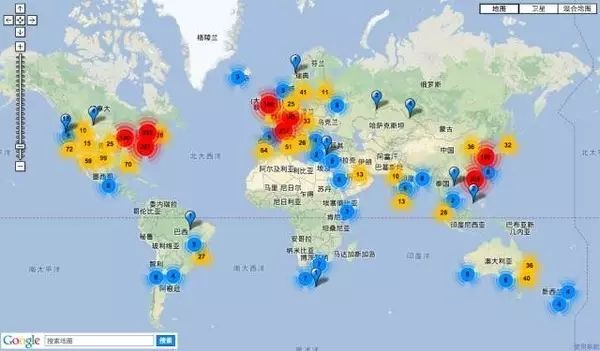
以下图10展示了当前全球测序仪的分布情况。图中的几个热点区主要分布在中国的深圳(主要是华大),南欧,西欧和美国。