蛋白质芯片的原理、分类及一般操作步骤(一)
概述
蛋白质芯片亦被称为蛋白质微阵列, 蛋白芯片的技术最早由Roger
Ekin在上世纪80年代就已提出,它是将大量蛋白质分子按预先设置的排列固定于一种载体表面形成微阵列, 根据蛋白质分子间特异性结合的原理,
构建微流体生物化学分析系统, 以实现对生物蛋白分子准确、快速、大信息量的检测, 是一种高通量、微型化和自动化的蛋白质分析技术. 简单地说,
就是一次试验中同时检测几百甚至几千种目标蛋白/多肽的分析技术.

基本原理
将各种蛋白质有序地固定于滴定板、滤膜和载玻片等各种载体上,然后,用标记了特定荧光的蛋白质或其他成分与芯片作用,
经漂洗将未能与芯片上的蛋白质互补结合的成分洗去,再利用荧光扫描仪或激光共聚焦扫描技术,
测定芯片上各点的荧光强度,通过荧光强度分析蛋白质与蛋白质之间相互作用的关系,由此达到测定各种蛋白质的目的.
固定在芯片上的蛋白可以是:抗原、抗体、小肽、受体和配体、蛋白质-DNA和蛋白质-RNA复合物等.
而抗体芯片是蛋白质芯片的主要类型,它的称谓来源于免疫学角度,由于其在微生物感染检测中巨大的潜在应用价值而引起人们广泛的兴趣,是蛋白质芯片研究中进展速度较快的一个分支。其主要检测方法有双抗体夹心法,样品标记法.
以Raybiotech公司的抗体芯片为例: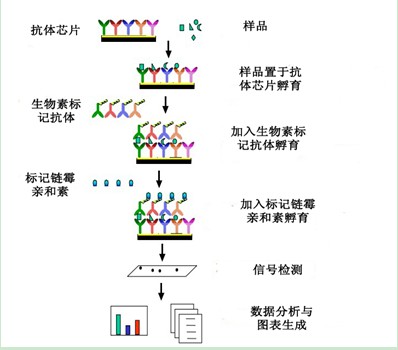
夹心法的原理图:
捕获抗体排列于膜或玻片上,加入样品孵育,再加入目标蛋白的生物素标记抗体,最后,HRP-链霉亲和素或荧光素-链霉亲和素用于检测芯片信号。