查看完整版本请点击这里:
【求助】pcr求助
各位大虾好,我再试验中遇到一些pcr困难,特向你们求助【求助】pcr求助
我自己设计的醛固酮合酶(CYP11B2)引物
F AGCGAGTGTTGGGTCCTCTGCT
R GAAAGCAACCTGCGGTCACAGGG
通过NCBI Primer-Blast 比对结果如下Primer pair 1
Sequence (5'->3') Length Tm GC%
Forward primer AGCGAGTGTTGGGTCCTCTGCT 22 59.85 59.09%
Reverse primer GAAAGCAACCTGCGGTCACAGGG 23 60.48 60.87%
>NM_000498.3 Homo sapiens cytochrome P450, family 11, subfamily B, polypeptide 2 (CYP11B2), nuclear gene encoding mitochondrial protein, mRNA product length = 566Forward primer 1 AGCGAGTGTTGGGTCCTCTGCT 22Template 2209 ...................... 2230Reverse primer 1 GAAAGCAACCTGCGGTCACAGGG 23Template 2774 ....................... 2752
[ 本帖最后由 moonlight45 于 2015-4-2 16:34 编辑 ]
查看完整版本请点击这里:
【求助】pcr求助
【求助】pcr求助
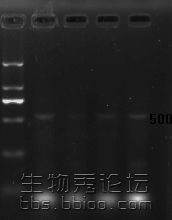
20min.jpg



最新回复
moonlight45 (2015-4-02 11:21:38)
1 我设计的该引物的产物是否就一定是醛固酮合酶(CYP11B2)?
2 我在摸索退火温度时第2次有目的条带,但浅谈,确定Tm56度,再次提取细胞RT-PCR2遍均后无目的片段表达
3 产物二聚体严重,怎样改进?
4肯请同行指点疑问,如能提供更好的引物,万分感谢。
vcve (2015-4-02 11:21:56)
你好,我也不太懂,只能说自己的看法,你设计的引物合成的并非全长酶基因,仅是其中一段。引物很合适,与模板完全匹配,应该没有问题。Tm值56度也比较合适。如果换我可能选60-55度做一梯度,看看那个温度是最佳的。至于你说的引物二具体,可以不用管它。在尝试几次好了!
abc816 (2015-4-02 11:22:12)
给lz几个建议,如果你按照ncbi的全基因序列设计引物的话,得到的应该改就是那个基因,用电泳检测带型大小与理论值相符就可以缺点他就是了,建议你再降低一下退火温度,最好做个梯度pcr,用nanodorp监测一下你的模板浓度,调整一下,另外你在加药的过程一定冰上进行,能减少一下引物二聚体的量
october7 (2015-4-02 14:23:07)
引物二聚体一般不用考虑
2541 (2015-4-02 14:26:45)
mickeylin (2015-4-02 14:27:22)
dog002 (2015-4-02 14:28:45)
vvmmoy (2015-4-02 14:29:06)
DCS (2015-4-02 14:29:28)
dior (2015-4-02 14:29:49)
退火温度相差1度,P出的结果明显不?
HOT兔 (2015-4-02 14:30:05)
用touch down跑跑看吧
moonlight45 (2015-4-02 14:30:26)
感谢上面各位老师的热心,我现在首要的问题是想明确我设计的引物出来的产物是否就是我要的目的。我将继续尝试各位的提议,再次致谢。
DCS (2015-4-02 14:30:59)
你的Blast好象不完全,怎么只有1个相近序列呀,一般Blast都会给出一大堆近似的序列的。或者跟你选择的比较范围有关吧。
如果实在没有底,可以先按照国外的文献做一下,这样剩点事。
gmt (2015-4-02 14:31:22)
JK.jon (2015-4-02 14:32:05)
iii_ii (2015-4-02 14:32:22)
youyou99 (2015-4-02 14:32:39)
引物二聚体影响不大,如果出现了目的片段,可以把PCR产物稀释,做二次PCR,就会出现比较亮的条带。
veiwu (2015-4-02 14:33:03)
PCR时可以加点DMSO试试看!
【求助】pcr求助