4D-组学新时代!更精确的磷酸化修饰组学


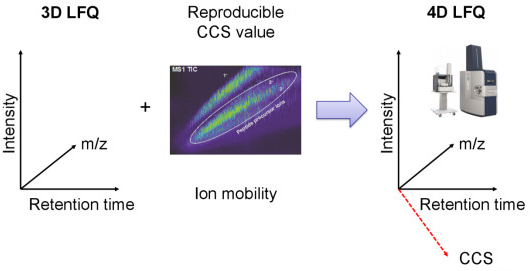
图1. 新一代4D-蛋白质组学示意图
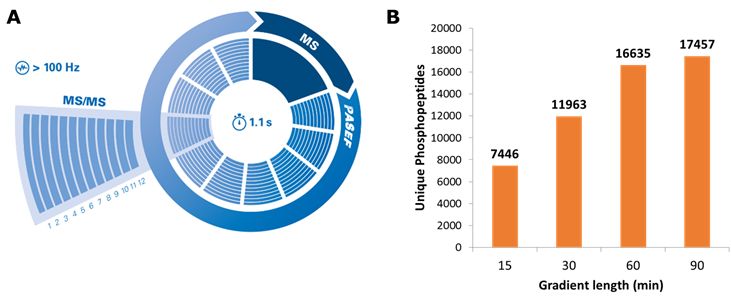
图2. A. timsTOF Pro单个扫描循环;B. 单针进样鉴定磷酸化修饰肽段数目
对于磷酸化肽段的同分异构问题,通过图3可以进行很好的解释,图3中的两个同分异构体的磷酸化肽段,分子序列完全一样,只是发生磷酸化的位置不同。这些同分异构的磷酸化肽段在一级谱图上的质量完全相同,而在二级谱图上也高度类似。面对这样微小的差别,传统的质谱鉴定和搜库软件通常难以做明确的区分,这就会导致出现错误定位(false localization)的问题。因此在处理PTM质谱数据时,需要对修饰位点进行FLR的控制。目前针对FLR的控制仍是一个挑战,主要是通过多种评估软件或算法来进行打分,但这些都是统计估算层面上的方法,并没有在质谱鉴定水平上解决修饰位点准确定位的问题。

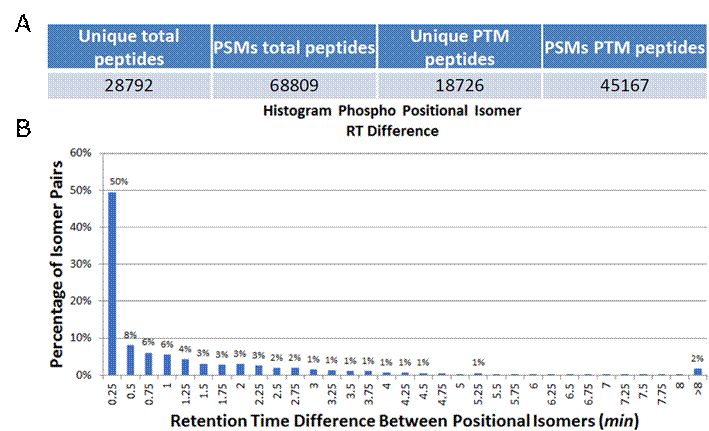
图4. 同分异构磷酸修饰肽段比例以及在不同保留时间的分布
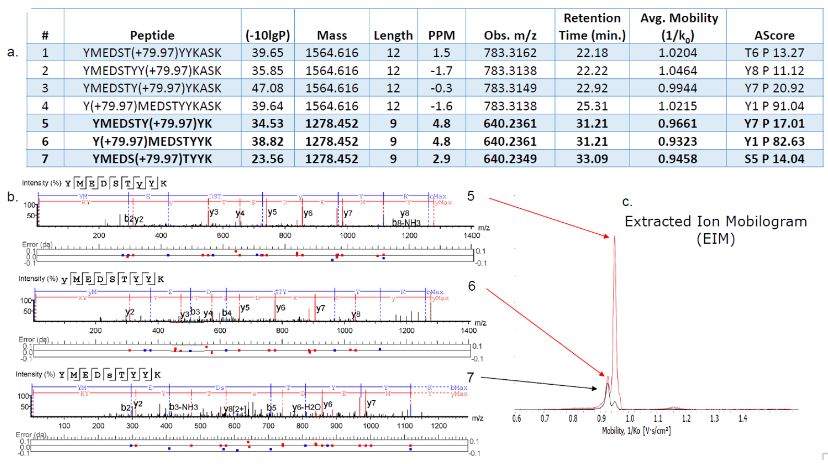
令人激动的是,新一代的4D-蛋白质组学除了在蛋白鉴定上有着卓越的性能,新增的离子淌度分离还能解决同分异构的问题,使得PTMs的鉴定更加可靠。图2中两个磷酸化肽段的同分异构体,尽管洗脱时间和质荷比完全一样,但是由于发生磷酸化的位置不同,所以在结构上会有差别,而4D-蛋白质组学的离子淌度分离会根据碰撞截面(Collision Cross Section,CCS)大小的不同对同分异构进行区分并获得可靠的磷酸化肽段的鉴定。
了解更多蛋白组学前沿技术,
请扫码领取A3海报样本!

参考文献:
1. Heiner Koch,et al., The PASEFmethod on a TIMS-QTOF mass spectrometer for High Sensitivity Phosphoproteomics.ASMS 2018, TP 555
2. Christopher M. Adams, et al., Identification and Quantitation of Phosphopeptide PositionalIsomers using Trapped Ion Mobility Spectrometry and PASEF. ASMS 2019, WP 662

-
微信文章

-
微信文章

-
微信文章

-
微信文章

-
微信文章

-
微信文章
-
微信文章

-
微信文章

-
微信文章

-
微信文章

-
微信文章
-
微信文章
-
微信文章

-
微信文章

-
微信文章

-
微信文章







