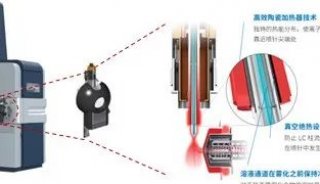
利用大规模肽碰撞截面(CCS)检测和深度学习研究4D-蛋白质组学


研究亮点
* 在timsTOF Pro系统上,通过捕集离子淌度(TIMS)和平行累积连续碎裂(PASEF)技术,获得了5种生物体蛋白质组全裂解液的100多万个CCS数据。
* 使用MaxQuant处理360多个LC-TIMS-MS/MS数据得到的大规模CCS数据。
* 通过CCS值比对,在重复测量的347885个肽段CCS值中,变异系数中值(CV)为0.4%,这表明了TIMS的CCS值在长时间、不同仪器间的运行中具有非常好的重现性。
* CCS数据的精确度(CV<1%)足以建立一个深度递归神经网络。该网络仅基于蛋白质基因组肽段序列便可以准确预测CCS值(R>0.99)。
这篇文章将timsTOF Pro上测得的CCS值作为肽段离子固有的重要特征,用于提高4D-鸟枪法蛋白质组学分析中肽段和蛋白质鉴定的可信度。由于基于质谱的蛋白质组学非常依赖获得谱图与蛋白质序列数据库的匹配准确度,因此准确的CCS值有利于缩窄候选列表。这对于在复杂基质,例如在血浆蛋白质组学、肽组学、免疫肽组学或宏蛋白质组学等需要准确测量低肽段信号的高灵敏度蛋白质组学来说至关重要。

图1:timsTOF Pro上测得CCS值的精确度、准确度与可利用度。


图3:使用TIMS和PASEF进行的大规模CCS测量。
a)通过消化,预分级,和色谱分离的全细胞蛋白质组的提取流程。以PASEF模式运行的TIMS-QTOF质谱仪。b)本研究中按生物体分类的CCS数据。c)肽段C末端氨基酸的频率。d)肽段N末端氨基酸的频率。e) 559,979个独特数据点的分布,包括修改序列和电荷分布,在CCS与m/z二维图按电荷状态进行颜色编码,CCS为纵坐标,m/z为横坐标,m/z和CCS的密度分布在顶部和右轴上。此数据为源数据文件提供。

-
微信文章

-
微信文章

-
微信文章

-
微信文章

-
微信文章
-
微信文章
-
微信文章

-
微信文章

-
微信文章
-
微信文章

-
微信文章

-
微信文章

-
微信文章

-
微信文章