解析DNA拓扑异构酶核心结构揭示DNA穿链新机制
生物物理所解析DNA拓扑异构酶核心结构揭示DNA穿链新机制成果入选Faculty of 1000 Biology


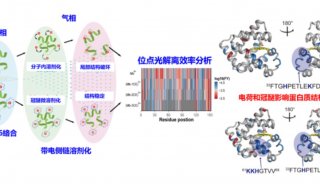
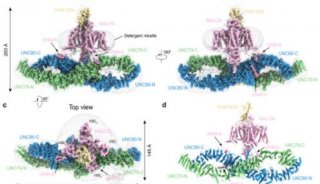
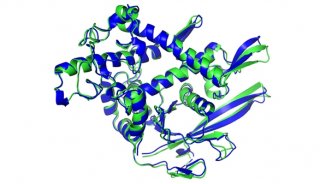
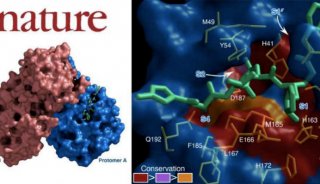
Gyrase B’三维结构(左)及结构域运动(右)
近日,中科院生物物理研究所王大成课题组与毕利军课题组合作在Nucleic Acids Research杂志上发表的题为Crystal structure of DNA gyrase B’domain sheds lights on the mechanism for T-segment navigation的研究论文获得Faculty of 1000 Biology的推荐和点评。此前,对于DNA链如何穿越到达待校正DNA这一基本的拓扑结构功能的动态过程的了解处于空白状态。该项研究结果解析DNA拓扑异构酶核心结构,揭示DNA穿链新机制,具有重要的基础理论意义。同时,由于Gyrase B’对病原菌的生存至关重要,其精细结构对提供研发广谱的相关药物,特别是抗生素的靶标,具有应用前景。
与有机体中多肽链折叠成蛋白质时常会出错相类似,DNA在细胞中重组、转录、复制、修复过程中也会发生错误,形成具有反常拓扑结构的“毒性”分子。如果不能纠正,细胞的正常功能会受到严重干扰,并可能导致死亡。因此,对其功能机制的研究是一个关系着原核生物正常生存的一个重要科学课题。
由于DNA的双链结构,其结构的错误类型和校正方式要比多肽链复杂许多。在包括各种病原菌在内的原核生物中,负责对DNA错位双链结构校正的是一类称为拓扑异构酶(Gyrase)的蛋白质分子,它是由三个基本部分构成的复杂分子机器,其核心是包含酶分子活性中心的部分,称为Gyrase B’。显然,这是保证细胞生存的基本蛋白质分子。Gyrase B’接受由酶分子N端通过ATP酶传递来的校正DNA链(T-segment),并需保证以正确的方位和取向输运到位于分子C端需要校正的拓扑错位DNA链(G-segment),最后完成DNA 的拓扑结构校正。DNA Gyrase B’发现已有30年历史,但此前对它的三维结构及如何完成功能作用的机制始终处于未知状态。
生物物理所王大成课题组与毕利军课题组合作,在2.8埃分辨率解析了结核杆菌DNA Gyrase B’的三维结构并揭示其作用机制,这是原核生物的第一个Gyrase B’结构。研究发现,Gyrase B’分子一个螃蟹状的新型二聚结构,深度的综合性结构分析结合一系列分子生物学突变实验揭示,该蟹状结构的“钳子”和“壳体”可在特定条件下发生“开合”运动(如图)。
在这一过程中,Gyrase B’分子调控、限定DNA链的正确方位和取向,以正常输运穿链DNA(T-segment)。同时发现,在DNA链与闭合的通道(“壳体”)间存在集中的负电荷,它们相互作用产生高能位,推动“通道”打开,如水闸导航船只过闸门一样。由此显示,在DNA拓扑异构酶分子机器中装载和输运DNA穿链采取一种特殊的“水闸模式”。由于Gyrase B’结构及其与功能关系的解析,使其有可能构建DNA拓扑异构酶Gyrase完整的分子机制,同时“水闸”模式的提出首次揭示DNA穿链可以通过Gyrase B’“导航”传递实现DNA拓扑结构校正的可能结构机理。
“Faculty of 1000 Biology”创办于2002年1月,是一种在线科研评价系统,其推荐原则立足于论文本身的科学意义而非发表在什么杂志上。该系统根据全球2300多名资深科学家的意见,提供对近期发表的生物科学论文的快速评论,目的是帮助广大科研人员遴选和发现有价值的研究工作。
-
焦点事件

-
项目成果
-
科技前沿

-
焦点事件

-
焦点事件

-
项目成果
-
焦点事件

-
科技前沿
-
综述
-
科技前沿

-
企业风采

-
产品技术

-
焦点事件

-
会议会展

-
企业风采
-
综述
-
科技前沿
-
焦点事件

-
项目成果
-
焦点事件

-
科技前沿
-
项目成果
-
焦点事件
-
焦点事件